Your new post is loading...

|
Scooped by
Life Sciences UPSaclay
September 9, 2019 6:11 AM
|
Lydie Kerdraon, récemment diplômée de l’ED ABIES, et des collègues phytopathologistes de l’unité INRA-AgroParisTech BIOGER viennent de publier dans la revue Microbiome les résultats d'une importante étude épidémiologique visant à caractériser la diversité microbiologique de résidus de blé. Les résidus laissés à la surface des champs après la récolte sont le siège de la reproduction sexuée du champignon Zymoseptoria tritici responsable de la septoriose du blé. L’étude, faisant appel à des techniques de metabarcoding (séquençage à haut débits de gènes « barcode »), confirme que les résidus sont un compartiment écologique particulièrement riche. Jusqu’alors négligé, ce compartiment mérite d’être pris en compte, dans un contexte où l’agroécologie tend à promouvoir les techniques culturales simplifiées (non labour). Les chercheurs ont caractérisé le microbiome (bactérien et fongique) associé aux résidus présents dans une parcelle de blé, avec et sans inoculation préliminaire de Z. tritici, en comparant un lot de résidus en contact avec le sol et un autre lot sans contact. Différentes analyses biostatistiques des données de métabarcoding (analyses discriminantes linéaires et analyses de réseaux d’interactions) ont illustré l’impact de la présence de l’agent pathogène sur les communautés microbiennes. L’analyse comparative des réseaux d’interactions a notamment permis d'identifier des taxons bactériens et fongiques, originaires à la fois du compartiment végétal et du sol, dont la présence est corrélée avec la présence de Z. tritici. Plusieurs de ces taxons avaient déjà été décrits comme « agents de biocontrôle » dans la littérature. L’étude suggère que les préserver, voire les exploiter, pourrait contribuer à améliorer les stratégies de protection des cultures contre certaines maladies fongiques. Contact : frederic.suffert@inra.fr

|
Scooped by
Life Sciences UPSaclay
September 15, 2019 10:20 AM
|
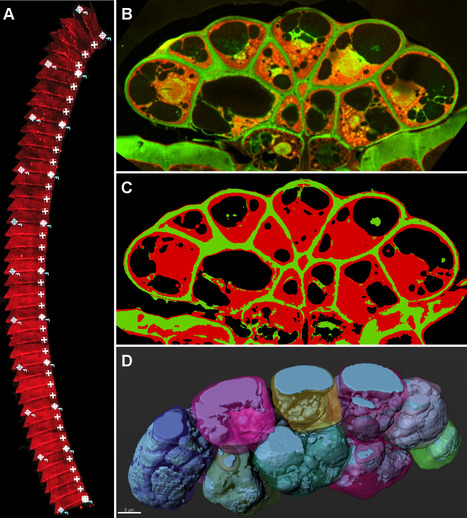
La Plateforme d’Imagerie Photonique (Institut de Biologie Intégrative de la Cellule – I2BC, Gif-sur-Yvette) donne accès à un parc de microscopes équipés pour répondre aux besoins d’imagerie de différents modèles cellulaires étudiés en biologie. Elle s’approprie régulièrement de nouvelles méthodes d’imagerie et met cette richesse d’expertise au service de la communauté scientifique de Paris-Saclay toute entière. Tout récemment, notre plateforme a développé un ensemble méthodologique permettant l’imagerie et la reconstruction 3D de gros volumes par microscopie confocale à balayage laser automatisée et l’analyse optimisée par une approche s’appuyant sur le « machine learning ». Contexte de ce développement et démonstration par l’image ! Les plantes carnivores subissent des remaniements majeurs de leur système endomembranaire lorsqu’elles entrent dans un processus de digestion, ce qui en fait un modèle d’étude idéal pour la morphologie des endomembranes. La microscopie électronique est alors la technique de choix pour les études morphologiques résolutives. Cependant elle s’avère longue et fastidieuse lorsqu’il s’agit d’imager de grands volumes comme des organes entiers. Dans notre cas, il s’agissait de glandes sécrétrices de Dionée, organes pour lesquelles typiquement des centaines de coupes sériées peuvent être réalisées (Figure A) après fixation chimique et enrobage en résine acrylique. Ces sections (250 nm d’épaisseur) peuvent être colorées puis imagées de manière automatique au microscope confocal à balayage laser (Figure B) permettant l’obtention d’images de très bonne résolution. Elles permettent également de séparer spectralement les composés fluorescents ou autofluorescents présents dans les différents compartiments cellulaires. Ces très grands volumes de données sont alors analysés par une approche de « machine learning » afin de détecter et segmenter automatiquement sur chaque image, les parois, le cytoplasme ainsi que les vacuoles (Figure C). Cette étape de segmentation automatique est d’autant plus facile que les marqueurs fluorescents sont discriminants spatialement et que les volumes de données sont importants pour « entrainer » le logiciel de machine learning. Enfin, ces données sont traitées par un logiciel de reconstruction des volumes (IMARIS) permettant d’extraire des objets et mesurer des volumes (Figure D). Ici, les données spectrales obtenues par microscopie confocale ont été essentielles pour permettre une reconnaissance automatique des compartiments cellulaires. Ce protocole d’analyse d’images a permis de mettre en évidence et de quantifier en 3 dimensions une forte fragmentation des vacuoles présentes dans le cytoplasme des cellules des glandes sécrétrices des plantes carnivores, lors du processus de digestion de proies. Ce travail a fait l’objet d’une communication par poster lors des 17èmes Journées du Réseau de Centres Communs de Microscopie (RCCM, aujourd’hui le RIME ou Réseau d’Imagerie en Microscopie Electronique) les 6, 7 et 8 juin 2018 à Clermont-Ferrand (Boulogne C et al., 3D analysis of secretory system in digestive glands of Venus flytrap). A noter : Ce travail a été mené en collaboration avec une autre plateforme d’Imagerie-Gif (I2BC) : la Plateforme de Microscopie Electronique (http://www.i2bc.paris-saclay.fr/spip.php?article282, Cynthia Gillet). Les différents systèmes d'imagerie de la Plateforme d’Imagerie Photonique permettent des approches multi-échelles allant du tissulaire (macroscopie), cellulaire (microscopie confocale) jusqu'au niveau subcellulaire (microscopie super résolue). La plateforme est hébergée au sein de l'Institut de Biologie Intégrative de la Cellule (I2BC), ce qui lui confère une forte expertise dans l'étude de différents modèles biologiques cellulaires : cellules animales, végétales, plantules, bactéries, levures… Afin de permettre aux utilisateurs d'exploiter au mieux les données obtenues sur les microscopes, ils sont également accompagnés par les ingénieur(e)s de la plateforme pour le traitement et l’analyse des images. Des stations de calcul puissantes équipées de logiciels dédiés sont mises à leur disposition. Certifiée ISO 9001 :2015/NFX 50-900 :2016, la plateforme accueille régulièrement des projets du secteur privé. Contact : romain.lebars@i2bc.paris-saclay.fr Plug In Labs Université Paris-Saclay : cliquer ici

|
Scooped by
Life Sciences UPSaclay
September 12, 2019 5:39 PM
|

|
Scooped by
Life Sciences UPSaclay
September 10, 2019 5:53 AM
|

|
Scooped by
Life Sciences UPSaclay
September 10, 2019 5:43 AM
|
Fête de la Science 2019 4, 5 et 6 octobre « LE VILLAGE DES SCIENCES PARIS-SACLAY» Gymnase du Complexe sportif de Gif-sur-Yvette Durant 3 jours, la fête de la science se déroulera dans un « Village des Sciences » qui rassemblera différents espaces dédiés à la science. Au fil des stands, vous pourrez expérimenter, tester, échanger et poser vos questions aux chercheurs et scientifiques du Plateau de Saclay venus à votre rencontre.

|
Scooped by
Life Sciences UPSaclay
September 9, 2019 6:25 AM
|
Le DIM1HEATLH lance un second appel à projets pour soutenir les projets d'investissement autour du concept One Health en infectiologie.
Montant : de 50 k€ à 1,6 M€
Date limite de candidature : 31 octobre 2019 à minuit

|
Scooped by
Life Sciences UPSaclay
September 8, 2019 10:24 AM
|
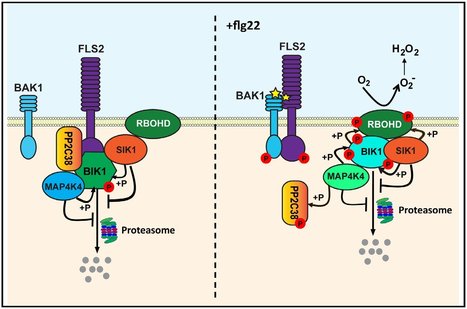
Les plantes peuvent percevoir dans leur environnement les pathogènes via des récepteurs transmembranaires qui reconnaissent des structures spécifiques du pathogène. Par exemple, la protéine flagelline, composant majeur du flagelle bactérien, est reconnue par le complexe de récepteurs FLS2-BAK1 ce qui induit une cascade de signalisation intracellulaire orchestrant les réponses de la plante. La protéine kinase cytoplasmique BIK1 est notamment activée par FLS2-BAK1 ce qui lui permet d’aller activer à son tour par phosphorylation la protéine RBOHD, responsable de la production d’espèces réactives de l’oxygène (ROS). Dans un article récemment publié dans EMBO reports, un travail collaboratif des équipes de Heribert Hirt (KAUST, Arabie Saoudite) et Jean Colcombet (IPS2 - Institut des sciences des plantes Paris-Saclay, INRA/UPSud/UEVE, Gif-sur-Yvette) montre que la protéine kinase MAP4K4, homologue de la protéine Ste20 de levure, joue un double rôle dans l’activation de BIK1. Tout d’abord, MAP4K4 phosphoryle directement BIK1, ce qui la stabilise. Mais elle phosphoryle également la phosphatase PP2C38, l’inhibiteur de BIK1, afin de promouvoir sa dissociation et renforcer l’activation de BIK1. Ces travaux permettent une meilleure compréhension des mécanismes de signalisation à l’œuvre lors des étapes précoces de la réponse immunitaire des plantes. Ils apportent également un nouvel éclairage sur les rôles de la famille multigénique MAP4Ks chez les plantes. Contact : jean.colcombet@inra.fr

|
Scooped by
Life Sciences UPSaclay
September 8, 2019 10:16 AM
|
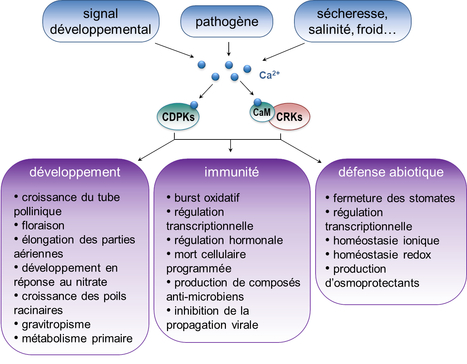
Le calcium est un second messager essentiel chez les plantes, dont les variations intracellulaires contrôlent de nombreux processus au cours du développement et en réponse aux contraintes environnementales. Les signaux calciques sont décodés par différents senseurs parmi lesquels les protéines kinases dépendantes du calcium (CDPKs) sont spécifiques des plantes et de certains protistes. Elles ont la particularité d’être directement activées par la fixation du calcium tandis que leurs plus proches homologues CRKs (CDPK-related kinases), incapables de lier le calcium, pourraient être stimulées par des senseurs relais comme la calmoduline. La plante modèle Arabidopsis thaliana possède 34 CDPKs et 8 CRKs, qui se distinguent par leurs profils d’expression, leur localisation et leurs propriétés biochimiques telles que la sensibilité au calcium, la spécificité de substrats, la régulation par phosphorylation ou par interaction avec des partenaires. Ces caractéristiques contribuent à la spécificité de la signalisation calcique, parallèlement à une certaine redondance fonctionnelle qui permet d’assurer la survie de la plante quelles que soient les conditions. Une revue parue dans New Phytologist par Tiffany Yip Delormel et Marie Boudsocq (Institute of Plant Sciences Paris-Saclay - IPS2, CNRS/INRA/UPSud/UEVE, Gif-sur-Yvette) résume les caractéristiques moléculaires de ces deux familles, ainsi que leurs implications dans le développement, les défenses immunitaires et les réponses aux stress abiotiques. Contact : marie.boudsocq@cnrs.fr

|
Scooped by
Life Sciences UPSaclay
September 5, 2019 3:39 PM
|
La pneumonie est la principale cause de mortalité des enfants dans le monde (http://perchresults.org). Une situation similaire existe pour les élevages bovins. Le virus respiratoire syncytial (VRS ou RSV en anglais) est le principal agent responsable des bronchopneumonies chez l’enfant et chez les veaux. Les vaccins bovins sont peu efficaces et il n’y en a pas pour l’homme. Le développement d’antiviraux représente une alternative qui pourrait sauver de nombreuses vies. Parmi les différentes cibles pour bloquer la réplication virale, l’ARN polymérase du virus est une cible de choix car spécifique du virus : ce complexe enzymatique n’a pas d’équivalent dans la cellule. Cette ARN polymérase dépendante de l'ARN est formée par la protéine L pour « large protein» associée à la phosphoprotéine virale tétramèrique (P). P remplit de nombreuses fonctions et est indispensable au fonctionnement de ce complexe polymérase. Malgré leurs rôles critiques dans la transcription et la réplication du RSV, les structures de L et P étaient jusqu’à présent inconnues. Une collaboration entre l’INRA de Jouy en Josas (Unité VIM, équipe Biologie Moléculaire des Pneumovirus), l’université du Texas, le CNRS (Université Aix-Marseille) et l’entreprise Janssen a permis de publier enfin la structure atomique de ce complexe P-L. Cette structure a été obtenue par cryo-microscopie électronique avec une résolution de 3.2 Å pour les connaisseurs. La structure révèle un arrangement tentaculaire saisissant de P dans lequel chacun des quatre monomères adopte une conformation distincte. La structure permet de comprendre le lien entre des mutations permettant au virus d’échapper à des inhibiteurs ou celles observées dans des vaccins candidats atténués vivants. Ces résultats fournissent un cadre irremplaçable pour la conception d'inhibiteurs efficaces contre le RSV. Contact : jean-francois.eleouet@inra.fr

|
Scooped by
Life Sciences UPSaclay
September 3, 2019 5:19 PM
|
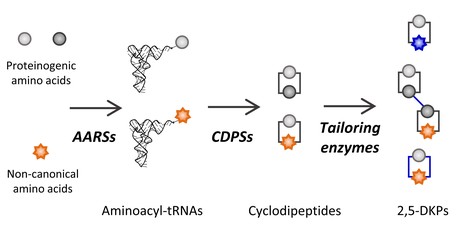
Les cyclodipeptides et leurs dérivés, appelés 2,5-dicétopipérazines (2,5-DKP), constituent une classe de produits naturels microbiens suscitant un grand intérêt en chimie médicinale car ils sont souvent dotés d’activités pharmacologiques remarquables telles qu’antibactériennes ou anti-cancéreuses. Dans une revue publiée récemment dans Natural Product Reports, les chercheurs de l’équipe Enzymologie et Biosynthèse Peptidique Non Ribosomique (I2BC/CEA, Gif-sur-Yvette) ont fait un point sur la connaissance des enzymes impliquées dans les voies de biosynthèse des 2,5-DKP et ont mis en lumière l’outil biotechnologique prometteur que constituent ces enzymes. La production des 2,5-DKP nécessite des acides aminés chargés sur des acides ribonucléiques de transfert (ARNt) par des aminoacyl-ARNt synthases (AARS). Ces molécules, les aminoacyl-ARNt, sont généralement dédiées à la machinerie ribosomique de synthèse des protéines mais des enzymes, les synthases de cyclodipeptides (CDPS), peuvent les détourner et les utiliser pour former des cyclodipeptides qui, à leur tour, peuvent être pris en charge par des enzymes de décoration introduisant une diversité de modifications chimiques. Grâce à l’élucidation de ces voies de production, l’équipe a pu fournir des acides aminés non canoniques chargés sur des ARNt aux CDPS qui ont alors synthétisé de nombreux cyclodipeptides non canoniques. Cette approche peut être combinée avec les différents travaux publiés par l’équipe mais aussi par d’autres équipes qui décrivent l’utilisation de différentes enzymes de décoration pour générer une grande variété de 2,5-DKP. La compréhension et la manipulation des voies de biosynthèse de produits naturels est une activité en plein essor qui devrait devenir incontournable grâce notamment aux progrès technologiques remarquables issus du domaine de la biologie synthétique. Contact : muriel.gondry@i2bc.paris-saclay.fr

|
Scooped by
Life Sciences UPSaclay
September 4, 2019 4:58 PM
|
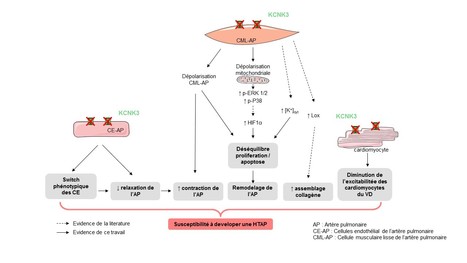
L’hypertension artérielle pulmonaire (HTAP) est une maladie cardio-pulmonaire sévère pour laquelle il n’existe actuellement aucun traitement curatif. Plusieurs mutations dans le gène KCNK3 ont été identifiées chez des patients atteints d’HTAP. Ce gène code pour un canal potassique, et les mutations décrites conduisent à une perte de fonction du canal. De plus, les chercheurs de l’UMR-S 999 (INSERM/UPSud, LabEx LERMIT, Centre Chirurgical de Marie Lannelongue, Le Plessis-Robinson) ont récemment montré que la dysfonction de KCNK3 (diminution de l’expression et/ou de la fonction) est commune à toutes les formes d’HTAP (idiopathique et héritable) ainsi que chez des modèles expérimentaux d’HTAP. Contrairement à l’homme et le rat, plusieurs études montrent que le canal KCNK3 n’est pas fonctionnel dans les cellules musculaires lisses des artères pulmonaires de souris, suggérant que la souris n’est pas un bon modèle pour étudier les conséquences de la perte de fonction de KCNK3 au niveau vasculaire pulmonaire. Dans l’objectif de mieux comprendre le rôle de KCNK3 dans cette maladie, Fabrice Antigny et son groupe de recherche dans l’UMR-S 999 ont étudié les conséquences de la perte de fonction de KCNK3 sur le développement de l’HTAP chez le rat. En utilisant la technologie CRISPR/Cas9 sur la plateforme de transgénèse de l’université de Nantes, une délétion de 94 pb a été introduite dans le premier exon du gène codant pour Kcnk3, induisant ainsi un décalage du cadre de lecture et l’apparition prématurée d’un codon STOP. Dans une étude qui vient de paraitre dans Circulation Research, réalisé dans le cadre du projet de thèse de Mélanie Lambert (ED569), les chercheurs ont regardé si la perte de fonction de KCNK3 était susceptible d’induire ou de faciliter le développement d’une HTAP chez les rats transgéniques. Ils ont obtenu les résultats suivants : - À l'âge de 4 mois, les rats mutés pour Kcnk3 développent une élévation spontanée de la pression systolique ventriculaire droite. Ces rats sont également plus sensibles aux inducteurs d’HTAP (monocrotaline ou exposition à l’hypoxie chronique).
- A l'âge à 12 mois, 25 à 45% de ces rats développent une hypertension pulmonaire spontanée.
- -Le dysfonctionnement de Kcnk3 conduit à une néomuscularisation des vaisseaux pulmonaires distaux, et à un dépôt de collagène périvasculaire, une sur-activation des voies de prolifération des cellules musculaires lisses des artères pulmonaires.
- Une augmentation de HIF1-α et ERK1/2 s’avère être les principaux événements moléculaires liés au dysfonctionnement de Kcnk3.
- Les artères pulmonaires de rats transgéniques présentent une plus forte sensibilité à la constriction et ils sont moins sensibles aux stimuli vasorelaxants.
- -Finalement, les cardiomyocytes du ventricule droit présentent une diminution d’excitabilité associée à un allongement de la durée des potentiels d’action.
L’ensemble de ces résultats révèle que la perte de fonction de KCNK3, in vitro et in vivo, contribue à la genèse de l'HTAP, et constitue un élément clef de cette pathologie (Figure). Ce modèle offre de nouvelles possibilités de compréhension des mécanismes initiateurs de l’HTAP. Contact : fabrice.antigny@u-psud.fr

|
Scooped by
Life Sciences UPSaclay
September 2, 2019 8:43 AM
|
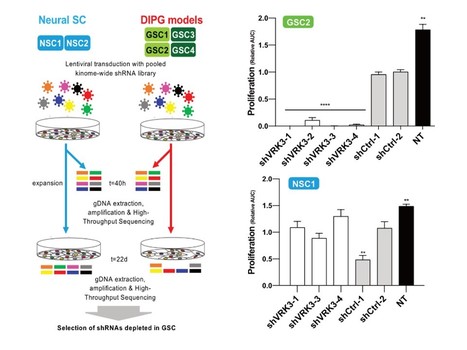
Dans une étude parue récemment dans Oncogene, Anne Debily et ses collaborateurs de l’UMR8203 (Vectorologie & Thérapeutiques Anticancéreuses, CNRS/Gustave Roussy/UPSud, Villejuif, France, et UEVE, Evry) ont réalisé un crible de léthalité synthétique à haut débit par ARN interférence afin de rechercher parmi les 700 kinase humaines les vulnérabilités des cellules de gliome infiltrant du tronc cérébral (DIPG). Cette tumeur, qui affecte les enfants entre 5 et 10 ans, reste aujourd’hui incurable et les rares mutations récurrentes retrouvées dans les patients ne peuvent être facilement ciblées. L’analyse par NGS a notamment montré que l’extinction de la protéine VRK3 (Vaccinia Related Kinase-3) était délétère pour les cellules tumorales, entravant leur prolifération et/ou leur survie, et ne l’était pas autant pour les cellules normales. Aucune altération de cette protéine n’a par ailleurs été identifiée dans ces tumeurs, reflétant l’intérêt d’une telle stratégie sans à priori. L’espoir d’une nouvelle opportunité thérapeutique est réel grâce à la découverte de cette vulnérabilité des DIPG même si des informations sur son mécanisme d’action et son rôle dans ces tumeurs seront nécessaires pour identifier ou développer un inhibiteur ciblé. Contact : marie-anne.debily@gustaveroussy.fr

|
Scooped by
Life Sciences UPSaclay
September 2, 2019 9:10 AM
|
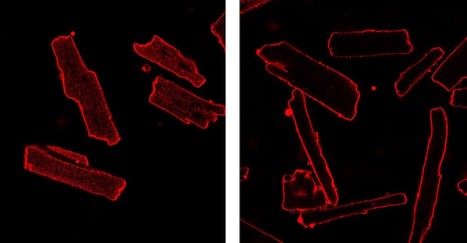
Les tubules en T sont des invaginations membranaires essentielles au couplage excitation-contraction des myocytes cardiaques, puisqu’ils permettent d’acheminer le potentiel d’action au plus profond du cardiomyocyte et de coordonner la libération du calcium contenu dans le réticulum sarcoplasmique qui permet la contraction de la cellule. Dans l’insuffisance cardiaque, on observe une diminution du nombre de ces tubules T, ce qui diminue l’efficacité du couplage excitation-contraction et conduit à des perturbations de l’homéostasie calcique pro-arythmiques qui accompagnent cette pathologie. Dans une étude récemment publiée dans Experimental Physiology, une équipe du laboratoire de Signalisation et Physiopathologie Cardiovasculaire (UMR-S 1180, INSERM/UPSud, LabEx LERMIT, Châtenay-Malabry) a exploré les effets de l'imipramine, un antidépresseur, qui est un médicament qui fait partie de la très grande famille des molécules amphiphiles cationiques. Ces composés sont connus pour interférer avec les interactions entre le phosphatidylinositol-4,5-bisphosphate (Pi(4,5)P2) membranaire et les protéines qui maintiennent le système tubulaire des cellules. Le but premier de cette étude était de valider cette molécule comme nouvel outil de recherche pour induire une « détubulation » des cardiomyocytes et permettre ainsi d’acquérir de nouvelles connaissances concernant le rôle de ces structures membranaires. Cela est chose faite, puisque ces travaux démontrent que l'imipramine, à fortes concentrations, est un très bon agent de détubulation des cardiomyocytes, qui s’avère plus efficace et moins toxique que le formamide, l’agent classiquement utilisé pour réaliser ces expériences. Mais ces travaux permettent également de mieux comprendre en quoi le Pi(4,5)P2 serait essentiel pour maintenir les tubules T attachés à la surface des cardiomyocytes et renseignent aussi sur les effets cardiotoxiques des surdoses d'imipramine qui s’accompagnent souvent d’une insuffisance cardiaque. Légende figure : Images confocales représentatives de myocytes ventriculaires de rats adultes témoins (panneau de gauche) et de cellules détubulées avec de l'imipramine (panneau de droite), marquées avec la sonde fluorescente lipophile, le di-4-ANEPPS. Contact : jerome.leroy@u-psud.fr
|

|
Scooped by
Life Sciences UPSaclay
September 15, 2019 5:30 PM
|
Des chercheurs de MIRCen montrent que l’inoculation d’extraits de cerveaux humains Alzheimer à des modèles primates induit des lésions typiques de la maladie ainsi qu’un processus neurodégénératif associé à des pertes de mémoire. Voir article dans Acta Neuropathologica Communications.. Contact : marc.dhenain@cea.fr

|
Scooped by
Life Sciences UPSaclay
September 15, 2019 10:06 AM
|
Le Conseil d’administration de la Société Chimique de France (SCF) a décidé de décerner Le Grand Prix Joseph-Achille Le Bel 2019 au Professeur Patrick Couvreur. Patrick Couvreur est reconnu au niveau international pour ses travaux dans le domaine de la vectorisation des médicaments pour le traitement du cancer. Il dirige une équipe au sein de l'Institut Galien Paris-Sud (UMR UPSud/CNRS 8612) à la Faculté de Pharmacie de l'UPSud à Châtenay-Malabry. La communauté des chimistes représentée par la SCF tient ainsi à saluer sa contribution précieuse au rayonnement de la Chimie, tout particulièrement son rôle pionnier dans le domaine de la vectorisation des médicaments, son rôle capital dans le domaine des nano-médicaments et la levée des verrous de l’encapsulation physique, ainsi, enfin, que pour son invention du concept de « squalénisation ». Toutes nos félicitations !

|
Scooped by
Life Sciences UPSaclay
September 10, 2019 6:03 AM
|
NETBIO est un réseau méthodologique créé au sein du département MIA de l'INRA depuis 2009 Sa vocation est de créer un espace pour (i) échanger sur les méthodes statistiques et bioinformatiques pour la construction et l'analyse de graphes (ii) discuter de la pertinence de ces modélisations pour étudier des relations de dépendances entre entités biologiques.
Depuis 2010, NETBIO organise des journées annuelles qui rassemble environ une quarantaine de personnes. Avec les années, il y a de plus en plus de biologistes qui souhaitent venir mais qui n'osent pas toujours, craignant d'assister à des exposés trop techniques C'est pourquoi cette année, NETBIO organise le lundi 14 octobre dans l'amphithéatre de l'IPS2 une journée pour découvrir des projets interdisciplinaires autour des réseaux Nous avons prévu 5 exposés d'une heure de duos biologiste/modélisateur afin que tous les aspects soient abordés.
Nous espérons attirer beaucoup de monde et en particulier des biologistes curieux de voir ce qu'il est possible de faire dans ce domaine.
Le programme est à découvrir ainsi que les moyens d’accès à l'IPS2 sur le site https://mia.toulouse.inra.fr/NETBIO Suivront les mardi 15 et mercredi 16, les journées NETBIO habituelles avec de la méthodologie, des applications et des discussions plus techniques que celles prévues le lundi.
NETBIO prend en charge les repas et les pauses, l'inscription est gratuite mais obligatoire. Afin de faciliter la logistique, pourriez-vous svp remplir ce sondage pour indiquer votre présence aux exposés et aux repas avant le 27 septembre https://evento.renater.fr/survey/netbio-2019-5te3i71u Au plaisir de vous y rencontrer Marie-Laure Martin-Magniette pour les organisateurs de NETBIO marie_laure.martin-magniette@agroparistech.fr

|
Scooped by
Life Sciences UPSaclay
September 9, 2019 7:51 AM
|
Conférence DHU HEPATINOV - 25/09/2019 - Pr Armelle DEBRU
Le Pr DUCLOS-VALLÉE ainsi que le Pr DEBRU ont le plaisir de vous convier à la conférence « La leçon d’Hippocrate est-elle encore pertinente dans un monde de biotechnologies ? », le Mercredi 25 Septembre 2019 à 15h00, au Centre Hépato-Biliaire Paul Brousse – 2ème étage – Amphithéâtre Pierre Barret – 12 avenue Paul Vaillant Couturier – 94800 Villejuif

|
Scooped by
Life Sciences UPSaclay
September 9, 2019 6:27 AM
|
La Fondation pour la recherche médicale lance un appel à projets "Environnement et santé".
Montant : 5 000 000 €

|
Scooped by
Life Sciences UPSaclay
September 8, 2019 10:52 AM
|
La plateforme AMATrace met à disposition des équipes du territoire Paris-Saclay un ensemble de tests comportementaux adaptés à des animaux modèles aquatiques permettant de mesurer locomotion, anxiété et stress, agression, mémoire spatiale et comportements sociaux. Les poissons téléostéens deviennent progressivement des animaux modèles pour les analyses comportementales, aussi bien pour l’analyse des comportements « innés » que pour des comportements « acquis ». Certains téléostéens possèdent un répertoire comportemental assez similaire à celui observé chez des mammifères et des oiseaux. Les bases neuroanatomiques chez les poissons modèles sont mal comprises mais leur avantage est la disponibilité des outils génétiques (e.g. poissons zèbres). La combinaison de ces approches avec les compétences de la plateforme permet d’aborder l’étude des mécanismes cérébraux des comportements. La plateforme AMATrace permet d’analyser les phénotypes comportementaux dans le cadre de projets de recherche grâce à ces nombreux protocoles standardisés. Exemple choisi de développement chez le poisson zèbre ! Récemment, une collaboration entre une équipe de l’Institut des Neurosciences Paris-Saclay (NEURO-PSI) et la plateforme AMATrace a permis la mise au point d’une méthode et un dispositif (aquarium dédié) permettant de mettre en évidence la mémoire de travail chez le poisson zèbre. Le test développé est une adaptation originale de celui couramment utilisé chez les mammifères ou les oiseaux (« delayed matching-to-sample » ou « choix après un délai en fonction d’un indice »), mais jamais à ce jour décrit pour le poisson. Il se base sur la règle suivante : « pour obtenir sa récompense, l’individu doit, après un délai de réflexion, choisir le compartiment possédant la couleur identique à celle présentée initialement ». Grâce à la création d’un protocole précis et d’un aquarium adapté nous avons pu obtenir des résultats montrant que le poisson zèbre est capable de faire non seulement un apprentissage associatif mais aussi de retenir une information pour s’en servir par la suite. Ces résultats ont fait l’objet d’une publication (Bloch et al., Behavioural Brain Research 2019) dans le cadre d’un travail de thèse de l’Université Paris-Saclay. De plus, en raison de l’innovation représentée par ce test et de ses possibilités d’applications variées (pharmacologique par exemple), une déclaration d’invention suivie d’un dépôt de brevet ont été effectués. Cette collaboration aura permis de mettre en place un protocole chez le poisson comparable à celui utilisé chez les mammifères et les oiseaux, permettant ainsi l’étude comparée d’une fonction cognitive comme la mémoire de travail. La plateforme AMATrace met à disposition une large panoplie de tests comportementaux adaptés à des modèles aquatiques tels que le poisson zébré, le Médaka et l’Astyanax, permettant de mesurer locomotion, fonction olfactive, ajustement sensori-moteur, anxiété et stress, agression, et mémoire émotionnelle et spatiale. L’équipement de cette plateforme a été financé par la Fondation pour la Recherche Médicale (FRM) dans le cadre de l’appel d’offres « Aide à la Création de Plateaux Techniques » 2008. Cette plateforme est opérée sous la direction d’un Ingénieur d’Etudes CNRS qui en assure maintenance et aide aux utilisateurs. Contact : cynthia.froc@inaf.cnrs-gif.fr Plug In Labs Université Paris-Saclay : cliquer ici

|
Scooped by
Life Sciences UPSaclay
September 8, 2019 10:45 AM
|
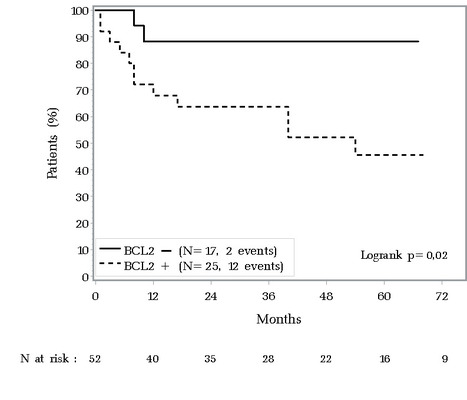
Le lymphome diffus à grandes cellules B (DLBCL) est le sous-type de lymphome le plus fréquent en population générale comme chez le patient infecté par le VIH. L'expression de BCL2, protéine anti-apoptotique, par les cellules lymphomateuses, est de mauvais pronostic en population générale mais sa valeur pronostique n'était pas établie chez les patients infectés par le VIH. Dans une étude multicentrique parue dans le British Journal of Haematology, dirigée par Caroline Besson de l’unité Hématologie-Oncologie du Centre Hospitalier de Versailles (UVSQ, Le Chesnay) et du Centre pour la Recherche en Epidémiologie et Santé des Populations - CESP (UMR-S 1018 INSERM/UPsud/UVSQ, Equipe "Générations et Santé" Gustave Roussy, Villejuif), les chercheurs ont mesuré l’expression de BCL2 par immunohistochimie sur des échantillons tumoraux provenant de patients atteints de DLBCL associé au VIH, inclus de manière prospective, entre 2008 et 2015, dans la cohorte française Lymphovir ANRS CO16. Parmi les 42 échantillons testés pour l'expression de BCL2, 25 étaient positifs. En analyse multivariée, l’expression de BCL2 était un marqueur pronostique péjoratif indépendant pour la survie sans progression à 4 ans qui était de 52% pour les patients dont le lymphome exprimait BCL2 versus 88% pour les autres patients (P=0,02, figure). Cette expression tendait à diminuer aussi la survie globale (63% versus 88%, P = 0,06). L’expression de BCL2 est donc un biomarqueur pronostique péjoratif indépendant dans le DLBCL associé au VIH. Ceci est un argument pour investiguer chez ces patients de nouvelles stratégies thérapeutiques basées notamment sur des inhibiteurs de BCL2. Contact : cbesson@ch-versailles.fr

|
Scooped by
Life Sciences UPSaclay
September 6, 2019 3:10 AM
|
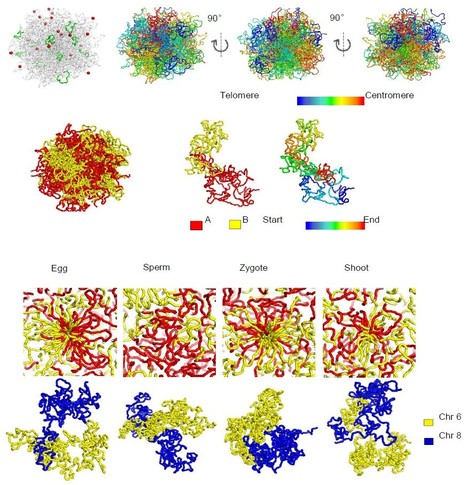
Spatial organization of chromatin structure plays an important role for genome function and epigenetic regulation of gene expression. Chromatin conformation capture (3C) and high throughput 3C (Hi-C) analyses allow studying three-dimensional (3D) genome structures in tissue or pooled samples through proximity ligation of DNA. Over the past years, 3D chromatin architecture in several plant species has been resolved by applying Hi-C technology to analyze pooled plant tissues. However, these 3D simulations are averages of large numbers of cells in the tissue samples and cannot display the 3D structure of individual cells. In a recent paper published in Nature Plants, Dao-Xiu Zhou and his colleagues at the Institute of Plant Sciences Paris-Saclay (IPS2, UPSud/CNRS/INRA/UEVE) developed a single cell Hi-C in plants and analyzed single cell 3D genomes of rice eggs, sperm and the unicellular zygotes as well as mesophylls. They found that the different cell types show overall a similar 3D genome structure but each cell has a different structure, indicating that the chromatin spatial structure is a dynamic system. The analysis reveals specific features of plant chromatin 3D structure in respect to spatial distribution of centromeres and telomeres, relatively few frequent chromosome folding and interaction between chromosomes compared with mammalian cells. In addition plant cells show a high level of gathering between similar functional chromatin domains which implies a coregulatory mechanism of gene expression. Important, the analysis uncovered a compact silent chromatin center in egg cells and zygotes which is dynamically remodeled after fertilization and is suggested to be involved in zygotic genome activation during early embryogenesis. Contact : Dao-xiu.zhou@u-psud.fr

|
Scooped by
Life Sciences UPSaclay
September 5, 2019 5:21 AM
|
Dans une revue parue dans Diabetes & Metabolism, Guy Fagherazzi (UMR-S 1018, INSERM/UPSud, Villejuif) fait le point sur les applications de la télémédecine dans la prévention et le traitement du diabète. Digital medicine, digital research and artificial intelligence (AI) have the power to transform the field of diabetes with continuous and no-burden remote monitoring of patients’ symptoms, physiological data, behaviours, and social and environmental contexts through the use of wearables, sensors and smartphone technologies. Moreover, data generated online and by digital technologies – which the authors suggest be grouped under the term ‘digitosome’ – constitute, through the quantity and variety of information they represent, a powerful potential for identifying new digital markers and patterns of risk that, ultimately, when combined with clinical data, can improve diabetes management and quality of life, and also prevent diabetes-related complications. Moving from a world in which patients are characterized by only a few recent measurements of fasting glucose levels and glycated haemoglobin to a world where patients, healthcare professionals and research scientists can consider various key parameters at thousands of time points simultaneously will profoundly change the way diabetes is prevented, managed and characterized in patients living with diabetes, as well as how it is scientifically researched. Indeed, the present review looks at how the digitization of diabetes can impact all fields of diabetes – its prevention, management, technology and research – and how it can complement, but not replace, what is usually done in traditional clinical settings. Such a profound shift is a genuine game changer that should be embraced by all, as it can provide solid research results transferable to patients, improve general health literacy, and provide tools to facilitate the everyday decision-making process by both healthcare professionals and patients living with diabetes. Contact : guy.fagherazzi@gmail.com

|
Scooped by
Life Sciences UPSaclay
September 5, 2019 4:23 AM
|
Increases of ambient temperatures affect plant growth and may have dramatic effects on plant architecture, biomass, and yield. Plants have evolved sophisticated regulatory mechanisms to acclimate to temperature increases by inducing adaptive elongation growth of stems and leaves to enhance cooling capacity and avoid heat flux. The molecular mechanisms such as gene expression reprograming of morphological changes are unclear. In a paper published in the Plant Journal, Dao-Xiu Zhou and his collaborators at the Institute of Plant Sciences Paris-Saclay (IPS2, CNRS/INRA/UPSud, Orsay) identified 3 chromatin regulators that function in the gene expression reprograming during plant response to increased ambient temperature. These chromatin regulators are histone deacetylases and gene transcriptional repressors. One of them, namely HDA15, directly represses the switch of gene expression at both normal and higher ambient temperature. HDA15 represses metabolic genes expression and accumulation of primary metabolites. HDA15 is targeted to the downstream genes by interacting with the transcription factor HFR1 (long Hypocotyl in Far Red1) to cooperatively repress plant response to high temperature. The results also indicate that metabolic genes expression and activity are involved in plant response to temperature increases. Contact: dao-xiu.zhou@u-psud.fr

|
Scooped by
Life Sciences UPSaclay
September 3, 2019 10:09 AM
|
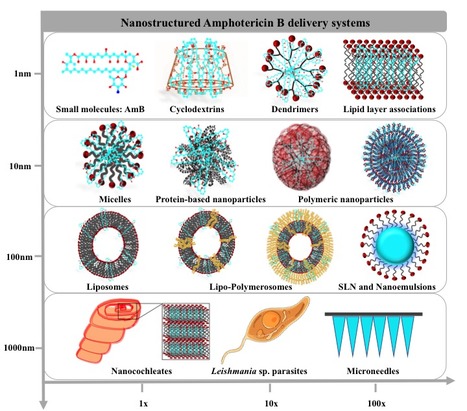
Parmi les médicaments en usage clinique pour le traitement des leishmanioses, l'amphotéricine B (AmB) est la molécule la plus active et a été la plus étudiée pour le développement de systèmes de vectorisation visant à diminuer sa toxicité. Ainsi, l'amphotericine B liposomale (AmBisome®) représente actuellement la meilleure option thérapeutique, cependant son efficacité clinique dépend du statut immunologique du patient et de la région d'endémie. Par ailleurs, son administration parentérale, ses effets secondaires et son coût élevé en limitent l'utilisation dans les pays en développement. Dans une revue publiée dans Expert Opinion on Drug Delivery, Philippe Loiseau (UMR8076 CNRS/UPSud, Faculté de Pharmacie, Châtenay-Malabry) présente une actualisation des stratégies nouvelles de vectorisation pour l'AmB sur les cinq dernières années, ainsi qu'une sélection critique des concepts émergents et des approches les plus prometteuses, basées sur des données d'activités précliniques et de toxicité. La faisabilité de libération de l'AmB par voies orale et topique a été démontrée sur des modèles animaux de leishmaniose, notamment via des nanovecteurs ciblant des ligands spécifiques et/ou des composants immunomodulateurs. Il reste à démontrer chez l'homme, la pertinence clinique de ces approches en terme d'efficacité, de toxicité et de coût pour une production industrielle à large échelle. Contact : philippe.loiseau@u-psud.fr

|
Scooped by
Life Sciences UPSaclay
September 2, 2019 8:19 AM
|
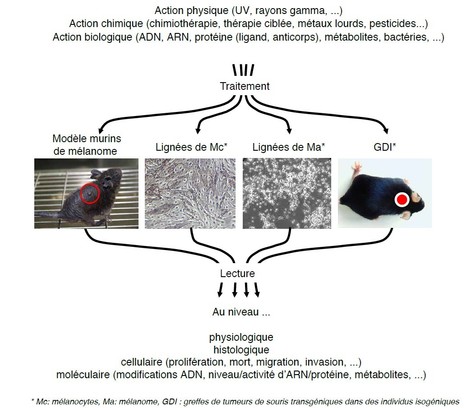
Dans un article paru récemment dans Pigment Cell & Melanoma Research, Lionel Larue, Valérie Petit et leurs collaborateurs de l’UMR3347/U1021 (INSERM/CNRS/UPSud/Institut Curie, Orsay) ont généré des lignées cellulaires de mélanome NRAS de souris sur un fond congénique C57BL/6, ainsi qu’un modèle génétiquement cohérent avec des souris transgéniques produisant des mélanomes cutanés (Ackerman et al., 2005; Delmas et al., 2007; Longvert et al., 2011), des mélanomes NRAS GDI (équivalent des PDX dans un environnement immunocompétent) et des lignées cellulaires normales de mélanocytes NRAS. Les chercheurs ont caractérisé le modèle aux niveaux moléculaire, cellulaire et oncogènique, et ont apporté la preuve de concept que ces lignées cellulaires peuvent être utilisées pour tester des thérapies ciblées. Précisément, ils ont montré que la combinaison d'inhibiteurs de MEK et d'AKT est très efficace pour arrêter la croissance des cellules de mélanome NRAS in vivo. Il est important de noter que ces lignées cellulaires peuvent être manipulées génétiquement pour générer des modèles plus sophistiqués. Sachant que la protéine NRAS n’est pas encore ciblable, il est important de générer des modèles pertinents pour tester efficacement de nouveaux médicaments et traitements. Cela inclut bien sûr également les thérapies immunitaires, puisque le modèle est sur un fond C57BL/6, des études appropriées seront effectuées dans ce sens. Légende Figure : Les animaux transgéniques (tg), les lignées de mélanocytes (Mc), les lignées de mélanomes (Ma) et GDI (les systèmes équivalent aux PDX [patient derived xenograft] dans un environnement immunocompétent) peuvent être soumis à des traitements physiques, chimiques et biologiques. Diverses lectures (physiologique, histologique, cellulaire et moléculaire) peuvent être effectuées. Contact : lionel.larue@curie.fr et valerie.petit@curie.fr
|



 Your new post is loading...
Your new post is loading...