Your new post is loading...

|
Scooped by
Life Sciences UPSaclay
Today, 12:47 PM
|
Ce jour, place à un FOCUS PLATEFORME sur Protopia, une nouvelle plateforme de prototypage avancé et de formulation d'ingrédients : un nouvel élément clé pour la bioéconomie Française ? Inaugurée le 28 mai 2025 par Valérie Pécresse, présidente de la Région Île-de-France, en présence de Stéphane Beaudet, président de Genopole, Protopia représente une avancée majeure dans le paysage biotechnologique français. Située sur le campus d'Évry-Courcouronnes, cette infrastructure lancée par Genopole est dédiée à l'accompagnement des projets biotech, de l'idée au prototype. Elle offre un environnement sécurisé et flexible pour la formulation et l'analyse de bio-ingrédients, servant les secteurs de la foodtech, de la cosmétique et des biomatériaux. Protopia s'intègre parfaitement dans le processus d'industrialisation des bioprocédés de fermentation, complétant ainsi l'infrastructure GATEX. Ce laboratoire de prototypage, équipé d'espaces modulaires de niveaux de confinement L1 et L2, est conçu pour soutenir les entreprises Biotech, les startups et les laboratoires du domaine de la bioéconomie. Il favorise non seulement les projets issus de la fermentation de précision mais aussi ceux basés sur des procédés d'extraction en chimie verte. En tant que pont entre la recherche fondamentale et le marché, Protopia s'inscrit dans la stratégie de Genopole et de Paris-Saclay pour créer un continuum territorial intégrant recherche, prototypage et production, renforçant ainsi une bioéconomie française responsable et autonome. Quelle est l’origine du nom ? Le terme Protopia renvoie à une vision réaliste et positive de l’avenir où le monde s’améliore progressivement. Contrairement à l’utopie (monde parfait) ou la dystopie (monde catastrophique), protopia décrit un futur meilleur mais imparfait marqué par des avancées lentes et continues. Quelles sont les missions de Protopia ? L’objectif premier de Protopia est d’offrir un cadre professionnel sécurisé pour transformer des ingrédients issus de procédés de fermentation en premiers prototypes. Il permet de tester la robustesse et la reproductibilité des prototypes, d’effectuer des analyses de qualité et d’ajuster les formulations avant leur industrialisation. Julien Picot, directeur adjoint délégué aux infrastructures et plateformes technologiques du GIP Genopole, souligne que « Protopia joue un rôle clé dans la chaîne d’innovation en fournissant un environnement maîtrisé pour transformer les bio ingrédients issus de fermentations de précision en prototypes industriels. Cette étape est essentielle pour garantir la qualité et la reproductibilité des produits avant la montée en échelle, et ainsi sécuriser les projets Biotech. Elle illustre parfaitement notre engagement à structurer une chaîne complète d’innovation, du laboratoire à l’industrialisation, en offrant aux acteurs de la biotech un environnement adapté pour développer et sécuriser leurs prototypes. C’est un levier majeur pour renforcer la compétitivité et la souveraineté de la filière bioéconomie ». Protopia joue également un rôle d’acculturation à la formulation industrielle pour les chercheurs et entrepreneurs, favorisant le passage du laboratoire au prototype commercial. Quels sont les équipements disponibles ? Le plateau analytique partagé de Protopia dispose d’équipements de pointe dédiés à l’analyse des formulations et de leur stabilité : texturomètre, viscosimètre, rhéomètre, réfractomètre, colorimètre, lyophilisateur, dessiccateur, tamiseuse… La cuisine professionnelle conforme aux normes HACCP permet la formulation d’ingrédients alimentaires. Quels sont les services proposés ? Les utilisateurs de Protopia bénéficient d’un accompagnement complet : accès à des boxs privés et espaces mutualisés, équipements d’analyses des formulations et de leur stabilité, appui d’un Lab Manager, et prestations sur mesure selon le stade de développement. Certains projets combinent prototypage, formulation, tests analytiques et ajustements itératifs pour structurer leur offre avant industrialisation. En savoir plus ? Destinée aux startups, PME et laboratoires académiques, Protopia fonctionne sur un modèle locatif : réservation des espaces nécessaires (box, cuisine, laboratoire de culture, plateau analytique, etc.), formation aux équipements par le Lab Manager et proposition de services annexes. Pour obtenir plus d’informations ou venir visiter Protopia, contactez-nous via Protopia@genopole.fr Protopia, un ancrage régional fort : Protopia constitue un maillon essentiel de l’écosystème Genopole et de Paris-Saclay, complétant GATEX, pour créer un continuum entre la recherche et développement, le prototypage et la montée en échelle. Installée au cœur de l’écosystème Genopole, Protopia est immédiatement connectée aux plateformes analytiques, réseaux d’experts, programmes d’accélération et aux financements régionaux. Cette articulation d’infrastructures traduit la vision conjointe de Genopole et de la Région d’un écosystème biotech intégré et souverain. Protopia participe à des initiatives européennes comme le consortium APROVALS, axé sur l’agriculture cellulaire, et s’ouvre à des partenariats internationaux pour accélérer l’innovation foodtech. À terme, Protopia vise à renforcer la compétitivité des startups dans les segments cosmétiques, biomatériaux et des protéines alternatives, un domaine émergent. -> Contact : Protopia@genopole.fr Plug In Labs Université Paris-Saclay : cliquer ICI GENOPOLE / PROTOPIA - Plateforme de prototypage avancé et de formulation d'ingrédients. Protopia est une plateforme de prototypage avancé inaugurée par Genopole pour accompagner les start-up biotech, en particulier dans les secteurs de la fermentation de précision. La force de Protopia repose sur une intégration multidisciplinaire : elle combine des laboratoires de culture cellulaire (niveaux L1 et L2), un laboratoire de microbiologie, des espaces dédiés à la formulation et à l’analyse des ingrédients issus de procédés biotechnologiques. Ces laboratoires permettent de concevoir, tester et affiner des prototypes de produits issus de la fermentation de précision, dans des conditions proches des marchés finaux (agroalimentaire, cosmétique, nutrition-santé). Protopia dispose également d’un plateau analytique sophistiqué, équipé de très nombreux équipements tels que texturomètre, rhéomètre, viscosimètre, colorimètre, réfractomètre, analyseur d’humidité, etc., ce qui permet d’évaluer rigoureusement les propriétés physico-chimiques (aspect, texture, stabilité…) des prototypes. En complément, une cuisine professionnelle (zone HACCP) est aménagée pour préparer des formulations alimentaires testables, avec des équipements industriels (fours mixtes, friteuses, etc.). Grâce à ce dispositif, les start-ups peuvent transformer un ingrédient issu d’un procédé biotech en produit pré-commercial, sans nécessiter des investissements trop lourds dès le départ, et en réduisant les coûts et délais liés à l’externalisation. L’approche collaborative et mutualisée de Protopia favorise les synergies entre entreprises, permettant des partenariats intersectoriels (foodtech, cosmétique, biomatériaux) autour de projets communs. Protopia dispose également de cinq box d’environ 10 m² chacun, pour offrir des espaces de travail flexibles et privés. Par ailleurs, Protopia joue un rôle stratégique dans la politique France 2030, en soutenant la bioéconomie durable et la transition vers des processus biotechnologiques plus propres et décarbonés. Elle offre également un accompagnement scientifique et business à ses usagers — des conseils pour la montée en échelle, la pré-industrialisation, et le prototypage sont disponibles pour les start-ups. L’ambition de Protopia est donc de combler un maillon essentiel dans la chaîne de valeur biotech : non seulement en validant des concepts moléculaires, mais aussi en leur donnant une forme de produit tangible, prête à être testée et commercialisée. Intégrée au cœur de l’écosystème Genopole, cette infrastructure renforce l’écosystème régional d’innovation et favorise l’émergence d’une filière biotech souveraine et durable. A propos de Genopole. Biocluster français dédié à la recherche en génétique et aux biotechnologies appliquées à la santé et à l’environnement, Genopole rassemble 78 entreprises de biotechnologies, 16 laboratoires de recherche, 23 infrastructures, plateformes et plateaux techniques mutualisés, ainsi que des formations universitaires (Université Évry Paris-Saclay). Son objectif : soutenir les entreprises de biotechnologies et le transfert de technologies vers le secteur industriel, favoriser le développement de la recherche dans les sciences de la vie, développer des enseignements de haut niveau dans ces domaines. Genopole est un Groupement d’intérêt public principalement soutenu par l’État, la Région Ile-de-France, l’agglomération Grand Paris Sud et l’AFM-Téléthon.

|
Scooped by
Life Sciences UPSaclay
May 26, 5:22 AM
|
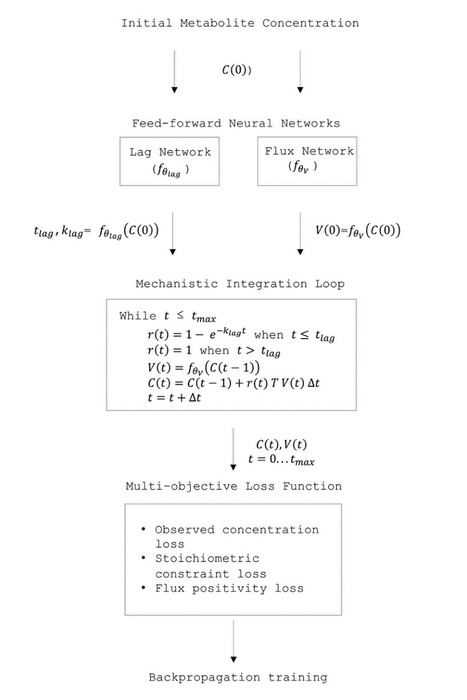
Dans une étude publiée dans Bioinformatics, des chercheurs de l’Institut Micalis (INRAE/AgroParisTech/UPSaclay, Jouy-en-Josas), en collaboration avec l'Université de Wageningen (Pays-Bas), ont développé dAMN (dynamic Artificial Metabolic Networks), un modèle hybride combinant réseaux de neurones artificiels et analyse dynamique des flux métaboliques à l'échelle du génome, pour prédire comment des bactéries croissent dans des environnements nutritionnels variés. Un défi central en biologie est de modéliser avec précision la croissance cellulaire en fonction de la composition du milieu de culture. Les approches mécanistes classiques peinent à se généraliser à de nouveaux milieux et ne capturent pas les phases de latence initiales — ce délai d'adaptation observable avant que les bactéries commencent à se diviser activement. dAMN surmonte ces limitations en intégrant des réseaux de neurones (ResNet) au sein d'un cadre contraint par la stœchiométrie du réseau métabolique complet de l'organisme. Entraîné sur des données de croissance d'Escherichia coli et de Pseudomonas putida dans des centaines de milieux combinatoires, dAMN prédit avec précision les dynamiques temporelles et se généralise à des milieux non vus lors de l'apprentissage (R² moyen ≥ 0,9). Le modèle reproduit spontanément des phénomènes biologiquement pertinents tels que la déplétion des substrats, le débordement d'acétate ou encore les croissances diauxiques — sans avoir été explicitement supervisé sur ces comportements. Le logiciel, les modèles et les données sont disponibles librement sur GitHub et Zenodo (DOI : 10.5281/zenodo.17908125). Légende Figure : Architecture de dAMN (figure tirée de l'article original). Le modèle combine deux réseaux de neurones — l'un prédit les paramètres de la phase de latence, l'autre les flux métaboliques — au sein d'une boucle d'intégration mécanistique contrainte par la stœchiométrie du réseau métabolique complet du microorganisme. L'ensemble est entraîné par rétropropagation en minimisant simultanément l'écart aux concentrations mesurées, les contraintes stœchiométriques et la positivité des flux. -> Contact : jean-loup.faulon@inrae.fr

|
Scooped by
Life Sciences UPSaclay
May 26, 5:36 AM
|
Relation entre les inhibiteurs calciques et le risque de maladie de Parkinson dans la cohorte E3N
Le repositionnement de médicaments existants représente une approche intéressante dans la maladie de Parkinson (MP) pour identifier des pistes de traitements qui pourraient permettre de ralentir l’évolution de la maladie voire de retarder son évolution. Les inhibiteurs calciques, qui sont principalement utilisés pour traiter l’hypertension artérielle et les pathologies ischémiques coronaires, représentent des candidats intéressants car les neurones dopaminergiques possèdent des canaux calciques de type L et que le calcium intervient dans les processus cellulaires conduisant à la mort cellulaire. Même si les études existantes sur les inhibiteurs calciques et le risque de MP rapportent des conclusions contradictoires, une méta-analyse a montré que les inhibiteurs calciques étaient associés à une réduction du risque de maladie de Parkinson. Les études antérieures souffrent toutefois de certaines limites, notamment le risque d’un biais de causalité inverse en raison de la longue phase prodromale de la maladie. Des études de cohorte avec un long suivi sont nécessaires pour prendre en compte ce biais. Une étude récente publiée dans Movement disorders, réalisée par Emilie Moutard, sous la direction d’Alexis Elbaz et Thi Thu Ha Nguyen au sein du Centre de recherche en Epidémiologie et Santé des Populations – CESP (UMR-S 1018 Inserm/UVSQ/UPSaclay, Villejuif), a étudié l’association entre la consommation d’inhibiteurs calciques et l’incidence de la maladie de Parkinson à partir des données de l’étude de cohorte E3N (Etude Epidémiologique auprès de femmes de l’Education Nationale), tout en tenant compte de la causalité inverse. Les nouveaux utilisateurs d’inhibiteurs calciques ont été identifiés à l’aide de bases de données de remboursement de médicaments à partir de 2004. Les chercheurs ont distingué les inhibiteurs calciques de type dihydropyridines (DiCCBs) des non-dihydropyridines (non-DiCCBs) et se sont aussi intéressés aux molécules les plus fréquentes. Les chercheurs ont utilisé des modèles de Cox à risque proportionnels pour variables dépendantes du temps, avec un décalage temporel de 5 ans entre l’exposition et l’incidence (lag) pour tenir compte de la causalité inverse ; des analyses de sensibilité sans lag et avec lag de 7 ans ont également été réalisées. De plus, les trajectoires d’utilisation des inhibiteurs calciques ont été décrites à l’aide d’un modèle logistique mixte au sein d’une étude cas-témoins nichée. Les analyses ont inclus 82 605 femmes, dont 603 ont développé une maladie de Parkinson et 13 022 ont consommé des inhibiteurs calciques. Les femmes ayant débuté un traitement par inhibiteurs calciques non-DiCCBs présentaient un risque plus élevé de MP que celles n’ayant jamais utilisé ce type de traitement (rapport de risque [RR] = 1.56, intervalle de confiance [IC] à 95% = 0.99-2.46 ; p de tendance = 0.02). Parmi les non-DiCCBs, le diltiazem était associé positivement à la MP (RR=2.20 [1.19-4.04]). Il n’existait pas d’association pour les inhibiteurs calciques en général, l’amlodipine et les non-amlodipine DiCCBs. Les analyses sans décalage temporel montrent une association de l’amlodipine (RR=1.45 [1.13-1.87]) et du diltiazem (RR=1.63 [1.02-2.60]) avec le risque de MP. L’ensemble des résultats sont cohérents avec les trajectoires de prescriptions d’inhibiteurs calciques chez les patients atteints de MP et les témoins. En conclusion, cette étude ne met pas en évidence d’effet protecteur des inhibiteurs calciques dans la MP. A l’inverse, les résultats pour le diltiazem et l’amlodipine concordent avec des cas rapportés dans la littérature de syndromes parkinsoniens induits pas certains inhibiteurs calciques à visées vasculaire, comme l’amlodipine, le diltiazem ou le verapamil, et d’autres inhibiteurs calciques utilisés dans le passé pour traiter les vertiges (flunarizine, cinnarizine). Ces syndromes parkinsoniens iatrogènes s’améliorent généralement après arrêt du traitement, mais il est aussi possible que ces médicaments aggravent les symptômes moteurs chez les femmes présentant une dénervation dopaminergique présynaptique préexistante et accélèrent ainsi le diagnostic de MP. Ces travaux justifient la nécessité de poursuivre les études et la surveillance sur les inhibiteurs calciques. -> Contact : alexis.elbaz@inserm.fr / emilie.moutard@inserm.fr

|
Scooped by
Life Sciences UPSaclay
May 26, 5:47 AM
|
Les télomères, situés à l’extrémité des chromosomes, jouent un rôle essentiel dans la préservation de l’intégrité du génome. Leur raccourcissement est associé au vieillissement cellulaire et à de nombreuses pathologies, ce qui rend cruciale la compréhension des mécanismes assurant leur stabilité. Dans un article publié dans Nature Structural & Molecular Biology, des chercheurs de l’UMR Stabilité Génétique, Cellules souches et Radiations - SGCSR (DRCM, UMR 1274 UPSaclay/INSERM/CEA-Jacob, Fontenay-aux-Roses) ont mis en évidence un nouveau mécanisme par lequel le recouvrement des télomères par une protéine spécifique les protège contre l’action du complexe Mre11-Rad50, impliqué dans la détection et la réparation des dommages à l’ADN. Ce recouvrement agit comme une barrière physique empêchant l’accès du complexe aux extrémités chromosomiques lorsque les télomères sont suffisamment longs. Cette découverte apporte un éclairage inédit sur la manière dont les cellules distinguent les télomères courts des télomères longs, un processus fondamental pour le maintien de la stabilité génétique et la régulation de la sénescence cellulaire. -> Contact : stephane.marcand@cea.fr

|
Scooped by
Life Sciences UPSaclay
May 26, 10:38 AM
|
Dans une étude publiée dans Science Advances les scientifiques du laboratoire Biologie des Pneumovirus de l’Unité Virologie et Immunologie Moléculaires – VIM (INRAE/UVSQ/UPSaclay, Jouy-en-Josas) ont étudié le rôle des trois protéines N, P, et M2-1 du virus respiratoire syncytial (VRS), dans les mécanismes de séparation de phase nécessaires à la formation et l’activité des usines virales dans la cellule infectée. Par une approche microfluidique PhaseScan (collaboration Université de Cambridge) permettant de contrôler finement les mélanges de protéines recombinantes purifiées, les auteurs ont déterminé les proportions optimales de protéines N et P, mais également confirmé le rôle de l’ARN, pour la formation de condensats in vitro. Les résultats obtenus ont en particulier mis en évidence pour la première fois l’importance de la protéine M2-1, qui favorise la formation de condensats en augmentant la multivalence. Ces résultats mettent en lumière les déterminants moléculaires de l'assemblage et de la formation de sous-compartiments au sein des usines virales du VRS, apportant un éclairage sur les mécanismes de réplication virale et ouvrant la voie à d'éventuelles stratégies antivirales ciblant ces processus de séparation de phase. -> Contact : marie.galloux@inrae.fr

|
Scooped by
Life Sciences UPSaclay
May 26, 5:10 AM
|
Portrait Jeune Chercheuse –Soumaya Najah, Maître de conférences en biologie de synthèse
Soumaya Najah a débuté sa carrière en tant qu’ingénieure en génie biologique. Elle poursuit rapidement son cursus par un Master de recherche, ensuite un doctorat au sein de l’équipe Microbiologie Moléculaire des Actinomycètes (MMA, I2BC, Université Paris-Saclay) sous la direction de Jean-Luc Pernodet. Ses travaux de thèse, dédiés à l’étude du métabolisme spécialisé d’une souche de Streptomyces, explorent la synthèse de produits naturels aux activités biologiques variées. Ces travaux se poursuivent par un premier post-doctorat dans la même équipe. Elle rejoint ensuite le Muséum national d'Histoire naturelle (MNHN) à Paris. Sous la direction de Yanyan Li, elle y approfondit son expertise sur le métabolisme microbien en se focalisant sur l’élucidation in vivo et in vitro des voies de biosynthèse de métabolites secondaires produits par le pathogène humain Pseudomonas aeruginosa. Soumaya Najah réintègre aujourd'hui l'Université Paris-Saclay en tant que Maîtresse de Conférences. Elle rejoint le département de Biologie de l’Université d’Évry Paris-Saclay. Elle intègre l’équipe « Ingénierie de la Fermentation », dirigée par Andrew Tolonen, au sein du Laboratoire de Génomique et Biochimie du Métabolisme LGBM à l’UMR 3080 Génomique Métabolique du Genoscope. Ses travaux de recherche actuels portent sur l’étude des adaptations métaboliques chez Clostridium phytofermentans, afin de favoriser une conversion efficace des sucres lignocellulosiques en alcools et en biomolécules à haute valeur ajoutée. Elle s’intéresse plus particulièrement à l’étude et à l’ingénierie des microcompartiments bactériens (BMCs), envisagés comme de véritables bio-nanomachines pour la fermentation lignocellulosique. Avec son statut d’enseignante chercheuse, Soumaya Najah partage désormais sa passion pour la science et son expertise en enseignant la microbiologie, la biologie moléculaire et la biologie de synthèse. Elle s'investit pleinement dans sa double mission de recherche et d’enseignement. Elle a à cœur de former les futurs talents de l'université tout en contribuant, par ses travaux de recherche, au rayonnement d'une bioéconomie durable et innovante. "I have learned that Success is to be measured not so much by the position that one has reached in life as by the obstacles which he has overcome while trying to succeed." - Booker T. Washington -> Contact : soumaya.najah@univ-evry.fr / snajah@genoscope.cns.fr

|
Scooped by
Life Sciences UPSaclay
May 28, 10:35 AM
|

|
Scooped by
Life Sciences UPSaclay
Today, 12:04 PM
|
Vendredi 15 mai 2026, 119 personnalités issues du monde de l’enseignement supérieur, de la recherche et de l’innovation ont été promues ou nommées à l’Ordre national du mérite. Sept d’entre elles font partie de la communauté de l’Université Paris-Saclay, dont quatre dans le domaine des SdV.
Au grade de chevalier
Abdelhafid Bendahmane, directeur de recherche INRAe à l’Institut des Sciences des Plantes Paris-Saclay - IPS2 (CNRS/INRAE/UEVE/UPSaclay, Gif-sur-Yvette), où il dirige l’équipe « Développement Floral et Déterminisme du Sexe » ; Purificación López-García, directrice de recherche CNRS au Laboratoire Ecologie Société Evolution - ESE (CNRS/UPSaclay/AgroParisTech, Gif-sur-Yvette) et membre de l’Institut de France ; Marie-Anne Rameix-Welti, chercheuse au Laboratoire Infection et Inflammation (2I) (UMR-S 1173 INSERM/UVSQ/UPSaclay) ; Régine Trebossen, directrice de recherche CEA et responsable animation secteur industrie de PASREL-imagerie (Univ. Paris-Saclay/CEA/CNRS/Inserm).

|
Scooped by
Life Sciences UPSaclay
Today, 11:23 AM
|
L'OncoSTART Entrepreneurship School c'est quoi ? Le consortium OncoSTART organise du 28 septembre au 02 octobre 2026 la 4ème édition de l’OncoSTART Entrepreneurship School dans les locaux du Paris Saclay Cancer Cluster (PSCC) à Villejuif. Cette semaine dédiée à l’entrepreneuriat en oncologie permettra à une quinzaine de participants de préciser et d’accélérer le business model de leur projet entrepreneurial. Prioritairement destinée aux porteurs de projet candidats à l’entrepreneuriat autour de la lutte contre le cancer au sens large, cette formation intensive a pour but d’aider les entrepreneurs et futurs entrepreneurs à comprendre les enjeux, les challenges et l’environnement de l’entreprenariat en oncologie à travers l’élaboration de leur business model. Ils s’appuieront sur les interventions de personnalités qualifiées aux profils variés (experts R&D, cliniciens, entrepreneurs, investisseurs, experts thématiques PI, RH, représentants de patients, etc.) qui leur fourniront à la fois les bases théoriques et l’opportunité de mise en pratique au travers des séances de coaching individuelles permettant de réussir à mener à bien leur projet entrepreneurial… REGISTER OBJECTIFS - Permettre aux participants de préciser et d’affiner le business model de leur projet entrepreneurial
- Apporter aux participants des outils, méthodologies et données appropriées pour maturer leur projet entrepreneurial
- Offrir aux participants des opportunités de faire grandir leur réseau
- Accompagner les participants dans la préparation d’un Pitch de présentation de leur projet.
A la fin de la semaine, chaque participant aura l’opportunité de présenter un pitch de son business model devant un panel de personnalités qualifiées et de profiter de leurs retours. Public Cible Cette formation est destinée aux porteurs d’un projet entrepreneurial autour de la lutte contre le cancer au sens large, toutes technologies deeptech (thérapie, diagnostic, dispositif médical, numérique/IA…). Les participants (étudiants, chercheurs, entrepreneurs) peuvent avoir créé leur start-up récemment ou bien avoir un projet entrepreneurial. Tarifs - 990€ HT pour les professionnels
- 490€ HT pour les étudiants
Des bourses peuvent être sollicitées de la part des membres fondateurs d’Oncostart pour soutenir certaines inscriptions, en fonction de vos organismes d’appartenance.

|
Scooped by
Life Sciences UPSaclay
Today, 11:45 AM
|
4th edition of the Symposium Maxime Dahan | Nov 30. - Dec. 1, 2026
We are pleased to announce the new edition of the Symposium in tribute to Maxime Dahan, entitled “Clusters and Condensates at the Cell Membrane” which will take place at Institut Curie.
The symposium will focus on phase separation, size regulation of membrane domains, biophysical aspects of membrane dynamics, as well as biochemical interactions within cells and at membranes. As the previous editions, this symposium is held in memory of Maxime Dahan, a pioneering biophysicist who passed away in 2018. It will bring together scientists from diverse disciplines to share their work and to continue his legacy in this exciting field of research at the interface of molecular cell biology and biophysics.
It features three scientific sessions with presentations by international scholars as well as selected short talks.
To be considered, please submit an abstract to: aida.fakhr@curie.fr.
Abstract deadline: September 30, 2026
The symposium will also be the occasion to award the Maxime Dahan Prize for Innovation in Methods and Instrumentation at the Interface of Physics, Biology & Medicine, funded by the Maxime Dahan fund.
📅 November 30 - December 1, 2026
📍 Constant-Burg amphitheater - 12 rue Lhomond, 75005 Paris
- Deadline for registration: November 10, 2026
- Sponsors: Institut Curie, LabEx DEEP, PSL-QLife, EnLife, EMBO
The organizing committee, Patricia Bassereau, Mathieu Coppey, Antoine Coulon, Aïda Fakhr, Bassam Hajj, Christian Specht (UMR-S 1195 Inserm/UPSaclay, Le Kremlin-Bicêtre).

|
Scooped by
Life Sciences UPSaclay
May 28, 10:38 AM
|
2,2 millions de patients sont concernés par les maladies inflammatoires chroniques de l’intestin (MICI). Le projet SUCCESS, porté par Philippe Langella (Institut Micalis INRAE/AgroParisTech/UPSaclay, Jouy-en-Josas) et Giovanna Oriane, en collaboration avec l’AP-HP Saint-Antoine, explore une approche innovante du microbiote. Soutenu et financé par la SATT Paris-Saclay, il vise à utiliser une bactérie bénéfique pour réduire l’inflammation intestinale et rééquilibrer l’écosystème. Des résultats précliniques prometteurs ouvrent la voie aux essais cliniques chez l’humain. En savoir plus -> Contact : philippe.langella@inrae.fr

|
Scooped by
Life Sciences UPSaclay
Today, 10:51 AM
|
Genopole devient membre fondateur du programme « Innovation Alliance Université Paris-Saclay » (IAUPS), dans le cadre du Pôle Universitaire d’Innovation (PUI) porté par l’Université Paris-Saclay.
Ce programme structurant, retenu en 2023 et financé à hauteur de 11 millions d’euros dans le cadre de France 2030, vise à accélérer le transfert de technologies, renforcer la recherche partenariale et soutenir l’émergence de start-up deeptech sur le territoire Paris-Saclay.
Le consortium fondateur du PUI rassemble notamment AgroParisTech, CentraleSupélec, CNRS, INRAE, Inria, Inserm, la SATT Paris-Saclay, IncubAlliance, l’Université Évry Paris-Saclay ou encore l’Université de Versailles Saint-Quentin-en-Yvelines. Lire la suite de l’Actu Genopole

|
Scooped by
Life Sciences UPSaclay
May 28, 11:24 AM
|
The goal of this program is to generate large-scale, high-resolution proteoform datasets across Parkinson's-relevant brain regions and matched biofluids to enable biomarker discovery and support the development of accessible, clinically meaningful fluid-based biomarkers.
|

|
Scooped by
Life Sciences UPSaclay
May 26, 5:15 AM
|
La résistance aux antibiotiques, en particulier aux β-lactamines, représente un enjeu majeur de santé publique. Le principal mécanisme de résistance repose sur l’hydrolyse de ces antibiotiques par des enzymes appelées β-lactamases. Certaines, les carbapénèmases, inactivent les carbapénèmes, antibiotiques de dernier recours contre les infections à bacilles à Gram négatif. En France, les carbapénèmases de type OXA-48 représentent 60,6% des entérobactéries productrices de carbapénèmases (EPC) isolées en 2022. Parmi elles, les variants R214G sont de plus en plus fréquemment détectés en France et dans le monde, bien que considérés comme des variants à perte de fonction et difficiles à détecter. En effet, la mutation R214G déstabilise le site actif de l’enzyme et réduit l’hydrolyse de plusieurs β-lactamines, notamment la témocilline et les carbapénèmes. Dans une étude récente publiée dans Antimicrobial Agents and Chemotherapy, les chercheurs de l’équipe RESIST de l’UMR-S 1184 (INSERM/UPSaclay/CEA et CHU de Bicêtre, Laboratoire de Bactériologie-Hygiène, AP-HP, Le Kremlin-Bicêtre), en collaboration avec l’Institut de Chimie des Substances Naturelles – ICSN (CNRS/UPSaclay, Gif-sur-Yvette), ont montré que l’utilisation de l’association pipéracilline-tazobactam, un antibiotique à large spectre fréquemment utilisé à l’hôpital, pourrait favoriser la sélection des variants R214G. En effet, une analyse fine des propriétés enzymatiques des variants R214G a montré que la plupart des β-lactamines sont moins bien hydrolysées, à l’exception de la pipéracilline, entraînant des hauts niveaux de résistance chez Escherichia coli. Les analyses enzymatiques et les modélisations structurales ont révélé que la substitution R214G améliore le positionnement et l’hydrolyse de la pipéracilline, conférant ainsi un avantage sélectif à ces variants. Légende Figure : Modélisation des interactions entre la pipéracilline et différents variants d’OXA-48 prédites par intelligence artificielle (Chai-1). (A, B) Interaction entre OXA-48 R214G (OXA-244) en vert) et la pipéracilline (cyan) : (A) représentation en surface de l’enzyme ; (B) représentation détaillée de la structure moléculaire. (C et D) Interaction entre OXA-48 (magenta) et la pipéracilline (rose) : (C) représentation en surface de l’enzyme ; (D) représentation détaillée de la structure moléculaire montrant des « clashes » avec le résidu R214, empêchant un positionnement optimal de la pipéracilline. (E) Positionnement de la pipéracilline dans le site actif d’OXA-48 : la pipéracilline (rose) présente des conflits avec le résidu R214. La position adoptée par la pipéracilline dans OXA-48 R214G (OXA-244) (cyan) est également représentée avec la surface d’OXA-48 (magenta). (F) Positionnement de la pipéracilline dans le site actif de OXA48 R214G (OXA-244) : la pipéracilline (cyan) peut se positionner plus facilement dans le site actif. La pipéracilline positionnée dans OXA-48 R214S (OXA-1167) (gris) adopte une conformation différente afin d’éviter les conflits avec le résidu S214. La surface de OXA-48 R214G (OXA-244) (bleu) avec G214 (orange). -> Contact : reva.nermont@universite-paris-saclay.fr

|
Scooped by
Life Sciences UPSaclay
May 26, 5:28 AM
|
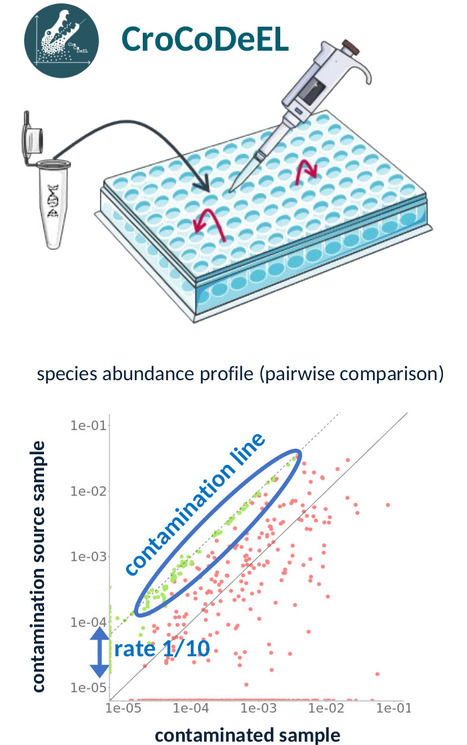
Le séquençage métagénomique permet de caractériser à haut débit des communautés microbiennes complexes telles que le microbiote intestinal humain. Cette approche demeure toutefois exposée à un biais technique majeur : la contamination croisée, un transfert accidentel d’ADN d’un échantillon à un autre lors des étapes de préparation en laboratoire. Non détectée, cette contamination conduit à attribuer à un échantillon des micro-organismes en réalité absents, compromettant la validité des résultats. Pour y remédier, des chercheurs des unités MetaGenoPolis et MaIAGE (INRAE/UPSaclay, Jouy-en-Josas) et de l'IRD ont développé CroCoDeEL, un logiciel dédié à la détection et à la quantification de telles contaminations. L'outil s'appuie sur l'analyse des profils d'abondance taxonomique afin d'identifier des signatures de transfert d’espèces entre échantillons, signe de contamination. Grâce à des approches combinant modélisation statistique et apprentissage automatique, CroCoDeEL permet d'en estimer le niveau (y compris à très faibles taux) et d’identifier l’échantillon source. Publiée dans Nature Communications, l'étude associée révèle des contaminations critiques passées inaperçues dans plusieurs travaux de référence fortement cités : certains transferts microbiens mère-enfant décrits dans la littérature relèveraient ainsi d'artefacts techniques plutôt que de transmissions biologiques avérées, invitant à une réévaluation de résultats antérieurs. Désormais librement accessible à la communauté scientifique internationale, CroCoDeEL constitue un dispositif de contrôle qualité simple pour renforcer la fiabilité des données métagénomiques et propose une interface web. Déjà adopté par plusieurs centres de recherche, il est mobilisé dans des projets d'envergure portés par l'INRAE, tel que French Gut, qui vise à cartographier le microbiote de 100 000 participants. -> Contact : emmanuelle.lechatelier@inrae.fr / guillaume.gautreau@inrae.fr

|
Scooped by
Life Sciences UPSaclay
May 26, 5:42 AM
|
Les vésicules intracellulaires jouent un rôle clé dans la biominéralisation en régulant la concentration et le transport du calcium, tout en maintenant l’homéostasie cellulaire. Bien que les vésicules chargées en calcium soient bien documentées chez les coccolithophores et les vertébrés, leur rôle dans la minéralisation des coquilles de mollusques reste à ce jour méconnu. Dans Communications Biology, des chercheurs du Laboratoire de physique des solides – LPS (CNRS/UPSaclay, Orsay) et de l’Université de Grenade ont étudié les mécanismes de transport du calcium chez Mytilus galloprovincialis. En combinant microscopie électronique et spectroscopie EELS, ils ont analysé trois types d’objets riches en calcium près de la surface de croissance de la coquille : des vésicules bilamellaires, des vésicules associées aux ribosomes et des mitochondries contenant des granules denses. Ces granules, qui contiennent également du phosphore, sont similaires à ceux observés dans les cellules osseuses des vertébrés, où ils jouent un rôle clé dans le stockage et le transport du calcium, conduisant à la formation de l’hydroxyapatite osseuse. Leur présence dans les cellules calcifiantes des mollusques et des vertébrés, combinée à des preuves croissantes de l’implication des phosphates dans la régulation des précurseurs transitoires du carbonate de calcium, suggère l’existence de mécanismes conservés entre des espèces phylogénétiquement éloignées, bien que les biominéraux formés diffèrent par leur composition (phosphate ou carbonate de calcium), leur structure et leur organisation. -> Contact : marta.de-frutos@universite-paris-saclay.fr

|
Scooped by
Life Sciences UPSaclay
May 26, 5:52 AM
|
Les systèmes acellulaires (Cell-Free System, CFS) basés sur des lysats reproduisent les fonctions cellulaires dans un environnement contrôlé. Ces outils polyvalents de biologie synthétique sont utilisés aussi bien pour la recherche fondamentale que pour la production de protéines ou le prototypage de circuits génétiques. Dans un article publié dans ACS Synthetic Biology, des scientifiques de l’équipe SyBER de l’Unité Micalis (INRAE/AgroParisTech/UPSaclay, Jouy-en-Josas) ont développé un CFS dérivé de la bactérie modèle à Gram positif Bacillus subtilis. Cette avancée repose sur l’utilisation d’un tampon à haute osmolarité permettant de reproduire l’environnement cytoplasmique de la bactérie. En effet, la pression osmotique interne de B. subtilis est trois à six fois plus élevée que celle de Escherichia coli, organisme modèle sur lequel la majorité des CFS ont jusqu’à présent été développés. L’étude montre, grâce à une analyse comparative et l’utilisation d’une bibliothèque de promoteurs, que la hiérarchie des forces promotrices est conservée entre les conditions in vivo et le CFS, validant cette plateforme comme modèle prédictif de la physiologie bactérienne. Les auteurs ont également reconstitué des régulations génétiques complexes en démontrant la répression fonctionnelle de promoteurs par un répresseur hétérodimérique activé in vitro via une cascade de phosphorylation. Enfin, ce tampon « haute osmolarité » a permis de faire fonctionner un CFS de Lactobacillus gasseri, une bactérie probiotique d’intérêt. Les CFS offrent ainsi un outil de criblage à haut débit, sur de faibles volumes réactionnels (10-15 µL), accélérant considérablement les tests de combinaisons génétiques par rapport aux approches in vivo. -> Contact : olivier.delumeau@inrae.fr / matthieu.jules@inrae.fr

|
Scooped by
Life Sciences UPSaclay
May 26, 10:44 AM
|
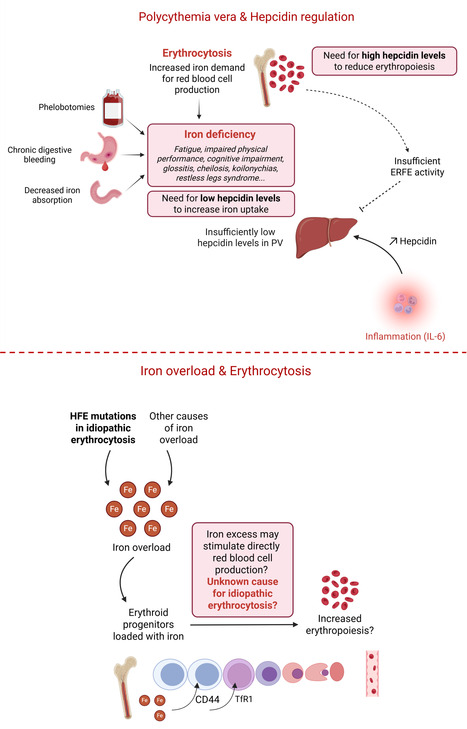
L'érythropoïèse et le métabolisme du fer sont étroitement interconnectés, aussi bien dans des conditions physiologiques que pathologiques. Cette relation complexe est explorée dans une revue publiée récemment dans Blood Cancer Journal par des chercheurs de l’UMR-S 1287 « Cellules souches hématopoïétiques et développement d'hémopathies malignes » (INSERM/UPSaclay/Gustave Roussy, Villejuif). La polyglobulie de Vaquez (PV) est une néoplasie myéloproliférative causée par une mutation de JAK2, entraînant une production incontrôlée de globules rouges. Dans la PV, la carence en fer est fréquente et peut résulter de plusieurs facteurs : saignements gastro-intestinaux chroniques, inflammation chronique induisant une élévation inadaptée de l'hepcidine, et saignées thérapeutiques. Paradoxalement, l'érythropoïèse clonale persiste malgré cette carence, contribuant à des symptômes invalidants (fatigue, troubles cognitifs, syndrome des jambes sans repos) qui altèrent la qualité de vie des patients. De nouvelles approches thérapeutiques, notamment les mimétiques de l'hepcidine ou les inhibiteurs de la ferroportine, visent à restaurer l'homéostasie du fer, améliorant la qualité de vie et réduisant potentiellement le recours aux traitements cytoréducteurs chez les patients porteurs d’une PV de faible risque. En dehors de la PV, il existe d’autres pathologies associées à une augmentation des globules rouges, ou érythrocytoses, pour lesquelles la cause n’est pas toujours retrouvée. Dans cette revue, les auteurs émettent l’hypothèse qu’une surcharge en fer pourrait en elle-même déclencher une production excessive de globules rouges. Des altérations de la régulation du métabolisme du fer pourraient constituer des causes méconnues d'érythrocytose. Une possible association entre érythrocytose et hémochromatose héréditaire, cause bien connue de surcharge en fer, reste insuffisamment comprise. -> Contact : guillemette.fouquet@gustaveroussy.fr

|
Scooped by
Life Sciences UPSaclay
Today, 12:14 PM
|
Marie-Anne Rameix-Welti, virologue, est nommée dans l'Ordre national du mérite au grade de Chevalier. C'est pour ses 19 ans de services que Marie-Anne Rameix-Welti, microbiologiste, professeure des universités-praticienne hospitalière, directrice d’une unité de virologie à l'Institut Pasteur a été promue par décret du Président de la République en date du 18 mai 2026.
Chercheuse au laboratoire Infection et Inflammation (2I - UMR 1173 - INSERM/UVSQ) de l'UFR Simone Veil - santé, Marie-Anne Rameix-Welti est virologue. Elle mène des recherches autour des virus. Elle a travaillé en collaboration avec des collègues du laboratoire Virologie et immunologie moléculaires (VIM) - UMR 0892 (INRAE/UVSQ) à un projet de sérologie sur la Covid-19 qui vise à rechercher des anticorps sur des sujets infectés et non-infectés. Cette recherche a été élargie aux quatre autres coronavirus saisonniers qui circulent chez l'homme depuis plus de deux siècles.
Ses travaux concernent notamment le virus respiratoire syncytial, plus communément appelé virus de la bronchiolite du nourrisson, et en particulier sur les mutations de résistance au nirsévimab qui se sont révélées très rares chez le VRS.
119 personnalités issues du monde de l’enseignement supérieur, de la recherche et de l’innovation, dont 68 femmes, parmi les promus ou nommés à l’ordre national du mérite, par quatre décrets du 15/05/2026, parus au Journal officiel du 18/05.
L'Ordre national du mérite, institution républicaine née au cœur du XXe siècle, est le second ordre national après la Légion d’honneur. Il a pour vocation de récompenser les « mérites distingués » et d’encourager les forces vives du pays. -> Contact : marie-anne.rameix-welti@uvsq.fr

|
Scooped by
Life Sciences UPSaclay
May 28, 11:15 AM
|

|
Scooped by
Life Sciences UPSaclay
May 28, 10:50 AM
|
Le « French SNOM user meeting » est un évènement annuel initié en 2022 autour de deux objectifs : structurer la jeune communauté française d’utilisateurs d’équipement SNOM (scanning near-field optical microscope) et partager les compétences et techniques développées par chacun. La montée en compétence de la communauté française permet désormais d’ajouter un objectif supplémentaire à cet évènement : faire rayonner les possibilités du SNOM dans de nouvelles communautés scientifiques. Cette 4ᵉ edition du « French SNOM user meeting » vise donc à rassembler la communauté et toutes les personnes qui pourrait être intéressé par cette technique au service de leurs recherches. Cette conférence gratuite (sur inscription) aura lieu du 23 au 24 Novembre 2026 dans l'amphithéâtre du Synchrotron Soleil et une visite d'installation est prévue le 25 Novembre 2026. Nous invitons tous ceux qui voudraient utiliser un microscope s-SNOM pour leurs sujets d'études à soumettre des abstracts en session poster. Inscription

|
Scooped by
Life Sciences UPSaclay
Today, 11:40 AM
|
Connecting Cohorts and Microbiomes
Only a few weeks before
the COHORTES-MICROBIOMES Annual Day! Friday June 26, 2026
Necker University, 160 rue de Vaugirard, Paris 15th
Secure your place now
Discover how large-scale cohorts are reshaping microbiome science, from everyday life to major clinical challenges, and meet national and European actors leading microbiome and cohort research. On the agenda for this annual event: - Morning session: Exploring the microbial landscape of everyday life and bridging health to disease
- Afternoon session: Uncovering diseases microbiome signatures for tomorrow prevention
Contact the COHORTES-MICROBIOMES Team! Scientific steering committee - Patrick Veiga (INRAE, Micalis, Jouy-en-Josas)
- Marion Leclerc (INRAE)
- Harry Sokol (AP-HP, Micalis, Jouy-en-Josas)
- Robert Benamouzig (AP-HP, et PNCA, Palaiseau)
- Nadine Cerf-Bensussan (Inserm)
- Karine Clément (Inserm)
-> Contact: benedicte.monnerie@inrae.fr

|
Scooped by
Life Sciences UPSaclay
Today, 10:29 AM
|
RAPPEL ! École d'Eté 2026 de l'OI HEALTHI - Innovation Thérapeutique - du 6 au 8 juillet 2026
L'Objet Interdisciplinaire Health and Therapeutic Innovation (HEALTHI) de l'Université Paris-Saclay organise son École d'Été "Innovation Thérapeutique". Pendant deux jours et demi des sujets variés seront proposés autour de l'innovation thérapeutique et du médicament avec des intervenants du domaine aussi bien académique qu'industriel. Le programme sera communiqué plus tard, mais vous pouvez envoyer votre candidature dès à présent. - Date: du 06 au 08 juillet 2026 (2,5 jours)
- Lieu: Domaine de Saint Paul à Saint-Rémy-Lès-Chevreuse en Île-de-France.
- Participantsdu monde académique ou privé (dans la limite des places disponibles) :
Doctorants, Post-doctorants,
Chercheurs, Enseignants-Chercheurs et Ingénieurs.
La participation à l’École d’Eté pourra être validée comme module d’enseignement pour les Doctorants. - Tarifs(inscription, hébergement et restauration) :
50 euros pour les Doctorants et Post-doctorants,
100 euros pour les Enseignants-Chercheurs et Chercheurs Académiques
300 euros pour le secteur privé. Dates clé : - Avant le 15 juin 2026 : Envoi du dossier de candidatures (CV et lettre de motivation) à l'adresse : healthi@universite-paris-saclay.fr
- Au plus tard le 18 juin 2026: Renvoi à chaque candidat de l'information relative à l'acceptation ou pas de sa candidature.
Pré-Programme (les intervenants mentionnés ont déjà donné leurs accords) L'industrie pharmaceutique : état des lieux et principaux enjeux François Ballet, MEDICEN Session Innovation thérapeutique dans le domaine de la dépression et des maladies neurodégénératives Denis David (INSERM), Delphine Joseph (CNRS) Session Innovation Thérapeutique dans le domaine cardiaque Marie-Christina Zennaro (INSERM), Mathias Mericskay (INSERM), Michel Azizi (AP-HP, CHU HEGP) Session « du développement à la clinique » Henri Caplain (EUFEMED), Marc Pallardy (Université Paris-Saclay), Lamie Grimaldi (CHU Raymond-Poincaré), Ségolène de Retz (Fondation A.R.CA.D) Session « L’environnement réglementaire et économique » Philippe Motté, CELESTIAL Consulting ; Isabelle BORGET (Institut Gustave Roussy, Université Paris-Saclay) Session « Transfert de technologies et valorisation des partenariats public-Privé » Mathieu Gutmann (SATT Paris-Saclay), Franck Mouthon (Inserm) Table-Ronde « Les métiers du médicament et de la santé après un doctorat » Raquel Diaz-Lopez (SATT Paris-Saclay), Joël Vacus (Drugabilis) Table-Ronde « Le recrutement et la recherche d’emploi métiers du médicament » Chantal Vernis (ABG -Association Bernard Gregory), Grégoire Prevost (CIPREVO), Stéphanie Blanc (GENSEARCH Consulting) L’école d’automne débutera à 9h30 le lundi 6 juillet pour se terminer le mercredi 8 juillet à 14h après le déjeuner.

|
Scooped by
Life Sciences UPSaclay
Today, 10:17 AM
|
Orano Med, filiale du groupe Orano et pionnière dans le domaine des alphathérapies ciblées en oncologie, a récemment inauguré son nouveau siège ainsi que ses nouveaux laboratoires de recherche et développement de pointe au sein du Paris-Saclay Cancer Cluster (PSCC), à Villejuif (Val-de-Marne). Cet évènement s’est déroulé en présence de Philippe Baptiste, ministre de l’Enseignement supérieur, de la Recherche et de l’Espace, de Nicolas Maes, directeur général d’Orano, de Frédéric Desdouits, directeur général d’Orano Med, ainsi que d’acteurs du projet et d’élus du territoire. Lire la suite de l’Article
🌍 CONFÉRENCE INTERNATIONALE Construire une carrière scientifique : de la recherche à l’innovation La Graduate School Health & Drug Sciences vous convie à une conférence internationale réunissant trois experts de renommée internationale. Une demi-journée pour explorer les grandes trajectoires scientifiques et les passerelles entre recherche, clinique et valorisation des innovations. 📅 15 juin 2026 ⏰ 10h00 – 12h30 📍 Amphithéâtre Henri Daniel (RDC – HM2) Université Paris-Saclay 🎯 Pourquoi participer ? Que vous soyez étudiant·e, doctorant·e ou jeune chercheur·e, cette journée vous permettra de : - Comprendre les débouchés des parcours scientifiques et clarifier vos perspectives de carrière
- Explorer les passerelles entre recherche, clinique et innovation
- Échanger avec des experts internationaux de premier plan
🔎 Trois thématiques clés au cœur des enjeux actuels - Construire une carrière académique à l’international
- Faire le lien entre recherche fondamentale et pratique clinique
- Transformer la recherche en innovation et en entrepreneuriat
🗓️ Programme 10h00 – 10h30 : Professeur Michael Drew Modérateur : Professeur Denis David Recrutement académique et structuration de la recherche à travers les mécanismes de la mémoire, de l’hippocampe et de la neurogenèse 10h30 – 11h00 : Professeur René Hen Modératrice : Professeure Delphine Joseph De la recherche fondamentale à la pratique clinique en psychiatrie – neurogenèse adulte et troubles psychiatriques 11h00 – 11h15 : Pause 11h15-11h45 : Professeur Etienne Sibille Modérateur : Professeur Jean-Philippe Guilloux Transformer la recherche en neurobiologie de la dépression en innovation thérapeutique et en projets entrepreneuriaux 11h45 – 12h30 : Table ronde interactive avec les doctorants et étudiants Discussion ouverte avec les trois professeurs Échanges autour des parcours, carrières et perspectives Thématiques : - Faire carrière en neurosciences aujourd’hui
- Passer du labo à la clinique ou à l’entreprise
- Mobilité internationale
- Financement et opportunités
12h30 – 14h00: Déjeuner & networking 🎓 Public : Étudiants · Doctorants · Enseignants chercheurs 📩 Inscription obligatoire jusqu'au 30 mai 2026
|






 Your new post is loading...
Your new post is loading...